Aproximaciones genómicas para identificar genes involucrados en enfermedades psiquiátricas
Resumen de Investigación:
La identificación de genes implicados en trastornos psiquiátricos es nuestra principal línea de investigación. Aunque los estudios de familias han constatado una fuerte contribución genética en la mayoría de estos trastornos, los genes involucrados permanecen por lo general desconocidos.
Ensayos a nivel de genoma completo indican que los trastornos psiquiátricos estén causados por una combinación de variantes genéticas comunes, cada una con un efecto modesto sobre el fenotipo, y variantes raras de mayor penetrancia.
En nuestro grupo combinamos distintas aproximaciones genómicas con el objetivo de identificar genes de susceptibilidad al trastorno del espectro autista (TEA), el trastorno bipolar y la esquizofrenia:
- Estudios de ligamiento genético: esta metodología tiene como objetivo mapear loci implicados en las enfermedades utilizando marcadores de ADN altamente polimórficos en familias con múltiples enfermos.
- Análisis de variantes del número de copias (CNV): pequeñas deleciones o duplicaciones de material genético (>50bp), particularmente las que incluyen genes, pueden representar factores etiológicos de la enfermedad.
- Estudios de asociación del genoma completo (GWAS) o genes candidatos: esta aproximación identifica polimorfismos de un solo nucleótido (SNP) (variantes comunes del ADN) que pueden estar asociados a la enfermedad.
- Secuenciación de nueva generación (NGS): la secuenciación del exoma completo (WES) o del genoma completo (WGS) permite identificar variantes de un solo nucleótido (SNVs) o variantes de novo (DN) (variantes raras del ADN), que pueden afectar la normal funcionalidad de las proteínas, aumentando el riesgo a padecer la enfermedad.
Nuestra experiencia en análisis de datos de alto rendimiento ha permitido la identificación de distintos genes en trastornos psiquiátricos: i) el gen DRP2, en el cromosoma X, forma parte actualmente de un panel para el test genético de autismo comórbido con discapacidad intelectual (ID); ii) el gen YWHAZ, implicado en autismo; iii) el gen IRS4, donde se identificó una mutación de parada prematura en una familia con pacientes esquizoafectivos; iv) mostramos la implicación de variantes comunes del gen LRP1 en esquizofrenia y de variantes raras en autismo; v) describimos que una carga elevada de variantes truncantes (alelos que causan la interrupción de la proteína) está asociada a una sintomatología más severa en autismo y trastorno bipolar, y que este tipo de variantes puede contribuir a modular funciones cognitivas; vi) hemos demostrado que los estudios de ligamiento son aproximaciones eficaces en enfermedades complejas cuando se combinan con secuenciación masiva.
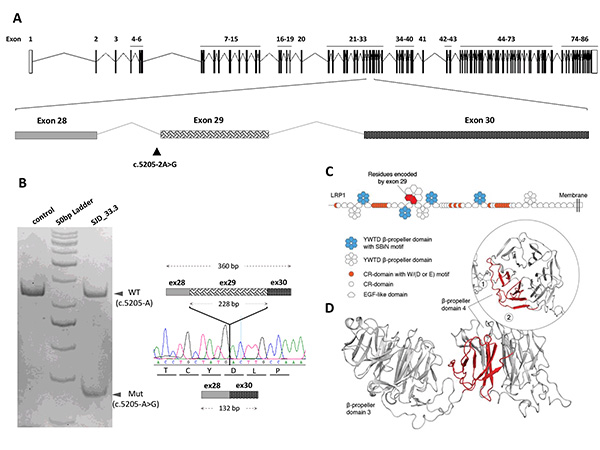
Figura 1. La secuenciación del exoma completo ha identificado una variante de novo con potencial efecto en el splicing del gen LRP1. (A) La variante esta indicada por un triangulo (c.5205–2A>G) entre el exon 28 y 30. Reacción a cadena de la polimerasa (PCR) sobre el transcrito mutado (Mut) ha identificado un fragmento más pequeño (132 bp) que carece del exón 29 (76 aminoacidos), y que genera un transcrito en pauta. (C) Dominios β-propeller de LRP1 como hexágonos. La región codificada por el exón 29 en el β-propeller-4 está en rojo. (D) La exclusión del exón 29 lleva a la remoción de las primeras dos de las seis laminas del β-propeller-4 (Torrico,…Toma (2019) Journal of Psychiatry and Neuroscience).
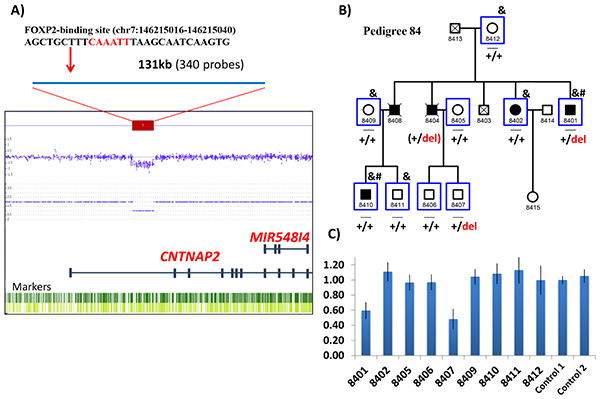
Figura 2. Deleción a lo largo del intrón 1 del gen CNTNAP2 en una familia extendida con trastorno bipolar. A) El Array muestra la reducción de señal de intensidad de las 340 sondas indicando la deleción en el paciente 8401. Es indicada la posición del sitio de unión de FOXP2 dentro de la deleción. B) La familia incluye cinco pacientes bipolares en dos generaciones. Individuos heterocigotos por la deleción están indicados con “+/del”. Experimentos de PCR cuantitativa (qPCR) han validado la deleción en el paciente 8401, y mostrado la deleción en el sujeto no afectado 8407.

| Apellidos | Nombre | Laboratorio | Ext.* | Categoría profesional | |
|---|---|---|---|---|---|
| Calzado González | Ángela | 415.5 | 4731 | Estudiante TFM | |
| Cendón Durán | Andrea | 415.5 | 4731 | Estudiante | |
| García Ortiz | Inés | 415.5.1 | 4731 | ines.garcia(at)cbm.csic.es | Ayudante Investigación |
| Martínez Jiménez | Miriam | 415.5 | 4731 | miriam.martinez(at)cbm.csic.es | Titulado Sup. Actividades Tecn. y Prof.GP1 |
| Rodríguez-Osorio Puigdueta | Cristina | 415 | 4731 | Estudiante TFM | |
| Ruggiero | Alessia | 415.5 | 4731 | Becario Erasmus | |
| Sánchez Moreno | Blanca | 415.5 | 4731 | Estudiante | |
| Somavilla Cabrero | Raúl | 415.5 | 4731 | rsomavilla(at)cbm.csic.es | M1 |
| Toma | Claudio | 415.5.1 | 4731 | claudio.toma(at)cbm.csic.es | Investigador |
Publicaciones relevantes:
- Mullins N, et al. (2021) Genome-wide association study of more than 40,000 bipolar disorder cases provides new insights into the underlying biology. Nature Genetics. doi:10.1038/s41588-021-00857-4.
- Toma Claudio*, Shaw AD, Heath A, Pierce KD, Mitchell PB, Schofield PR, Fullerton JM*. (2021) A linkage and exome study of multiplex families with bipolar disorder implicates rare coding variants of ANK3 and additional rare alleles at 10q11-q21. (*, corresponding authors) Journal of Psychiatry and Neuroscience 46(2):E247-E257. doi: 10.1503/jpn.200083.
- Torrico B, Antón-Galindo E, Fernàndez-Castillo N, Rojo E, Ghorbani S, Pineda-Cirera L, Hervás A, Rueda I, Moreno E, Fullerton JM, Casadó V, Buitelaar JK, Rommelse N, Franke B, Reif A, Chiocchetti AG, Freitag C, Kleppe R, Haavik J, Toma Claudio* and Cormand B*. (2020) Involvement of the 14-3-3 gene family in autism spectrum disorder and schizophrenia: genetics, transcriptomics, and functional analyses. Journal of Clinical Medicine. doi.org/10.3390/jcm9061851. *, joint senior and co-corresponding authors.
- Toma Claudio, Shaw AD, Overs BJ, Mitchell PB, Schofield PR, Cooper AA, Fullerton JM. (2020) Coding De novo Variants in Multiplex Bipolar Families are Implicated in Disease Liability. doi: 10.1001/jamanetworkopen.2020.3382 JAMA Network Open; 3(5): e20338216.
- Toma Claudio* (2020) Genetic variation across phenotypic severity of autism. Trends in Genetics 36(4):228-231 doi.org/10.1016/j.tig.2020.01.005 (*, corresponding author)
- Toma Claudio, Díaz-Gay M, Soares de Lima Y, Arnau-Collell C, Franch-Expósito S, Muñoz J, Overs B, Bonjoch L, Carballal S, MD PhD, Ocaña T, Cuatrecasas M, Castells A, Bujanda L, Cubiella J, Balaguer F, Rodríguez-Alcalde D, MD PhD, Fullerton JM, Castellví-Bel S (2019) Identification of a novel candidate gene for serrated polyposis syndrome by performing linkage analysis combined with whole-exome sequencing. Clinical and Translational Gastroenterology
- Toma Claudio, Díaz-Gay M, Franch-Expósito S, Arnau-Collell C, Overs B, Muñoz J, Bonjoch L, Soares de Lima Y, Ocaña T, Cuatrecasas M, Castells A, Bujanda L, Balaguer F, Cubiella J, Caldés T, Fullerton JM, Castellví-Bel S (2020) Using linkage studies combined with whole-exome sequencing to identify novel candidate genes for familial colorectal cancer. International journal of Cancer 15;146(6):1568-1577. doi: 10.1002/ijc.32683
- Torrico B, Shaw AD, Mosca R, Vivo-Luque, Hervas A, Fernàndez-Castillo N, Aloy P, Monica B, Fullerton JM, Cormand B, Toma Claudio*. (2019) Truncating Variant Burden in High Functioning Autism and Pleiotropic Effects of LRP1 Across Psychiatric Phenotypes. doi: 10.1503/jpn.180184 Journal of Psychiatry and Neuroscience 16; 44:1-10. (*, corresponding author)
- Toma Claudio*, Pierce KD, Shaw AD, Heath A, Mitchell PB, Schofield PR, Fullerton JM (2018) Comprehensive cross-disorder analyses of CNTNAP2 suggest it is unlikely to be a primary risk gene for psychiatric disorders. PLoS Genetics Dec 26;14(12):e1007535. doi: 10.1371/journal.pgen.1007535 (*, corresponding author)
- Brandler BM, Antaki D, Gujral M, Kleiber ML, Whitney J, Maile MS, Hong O, Chapman TR, Tan S, Tandon P, Pang T, Tang SC, Vaux KK, Yang Y, Harrington E, Juul S, Turner DJ, Thiruvahindrapuram B, Kaur G, Wang Z, Kingsmore SF, Gleeson JG, Bisson D, Kakaradov B, Telenti A, Venter J C, Corominas R, Toma Claudio, Cormand B, Rueda I, Guijarro S, Messer KS, Nievergelt CM, Arranz MJ, Courchesne E, Pierce K, Muotri AR, Iakoucheva LM, Hervas A, Scherer SW, Corsello C, Sebat J (2018) Paternally inherited cis-regulatory structural variants contribute to autism. Science Apr 20;360(6386):327-331. doi: 10.1126/science.aan2261.
- Toma Claudio, Shaw AD, Allcock RJN, Heath A, Pierce KD, Mitchell PB, Schofield PR, Fullerton JM (2018) An Examination of Multiple Classes of Rare Variants in Extended Families with Bipolar Disorder. Translational Psychiatry. 13;8(1)65.
- Torrico B, Chiocchetti AG, Bacchelli E, Trabetti E, Hervás A, Franke B, Buitelaar JK, Rommelse N, Yousaf A, Duketis E, Freitag CM, Caballero-Andaluz R, Martinez-Mir A, Scholl FG, Ribasés M; ITAN, Battaglia A, Malerba G, Delorme R, Benabou M, Maestrini E, Bourgeron T, Cormand B, Toma Claudio*. (2017) Lack of replication of previous autism spectrum disorder GWAS hits in European populations. Autism Res. 10:202-211. (*, corresponding author)
- Toma Claudio*, Torrico B, Hervás A, Salgado M, Rueda I, Valdés-Mas R, Buitelaar JK, Rommelse N, Franke B, Freitag C, Reif A, Pérez-Jurado LA, Battaglia A, Mazzone L, Bacchelli E, Puente XS, Cormand B. (2015) Common and rare variants of microRNA genes in autism spectrum disorders. World J Biol Psychiatry. 23:1-11 (PMID: 25903372) (*, corresponding author)
- Torrico B, Fernàndez-Castillo N, Hervás A, Milà M, Salgado M, Rueda I, Buitelaar JK, Rommelse N, Oerlemans AM, Bralten J, Freitag CM, Reif A, Battaglia A, Mazzone L, Maestrini E, Cormand B, Toma Claudio*. (2015) Contribution of common and rare variants of the PTCHD1 gene to autism spectrum disorders and intellectual disability. Eur J Hum Genet. 23: 1694-701. (*, corresponding author)
- Toma Claudio, Torrico B, Hervás A, Valdés-Mas R, Tristán A, Maristany M, Padillo V, Romarís P, Arenas C, Puente X, Bayés M, Cormand B (2014) Exome sequencing in multiplex autism families suggests a major role for heterozygous truncating mutations. Mol Psychiatry. 19: 784-90.
Tesis doctorales:
- Dr Barbara Torrico Avilés (Universitat de Barcelona, 2012-2015): Genética molecular del autismo: identificación de variantes de susceptibilidad y estudios funcionales (Co-direccion con Prof. Bru Cormand).




















